R语言实现常用的5种分析方法(主成分+因子+多维标度+判别+聚类)
R语言多元分析系列之一:主成分分析
主成分分析(principal components analysis, PCA)是一种分析、简化数据集的技术。它把原始数据变换到一个新的坐标系统中,使得任何数据投影的第一大方差在第一个坐标(称为第一主成分)上,第二大方差在第二个坐标(第二主成分)上,依次类推。主成分分析经常用减少数据集的维数,同时保持数据集的对方差贡献最大的特征。这是通过保留低阶主成分,忽略高阶主成分做到的。这样低阶成分往往能够保留住数据的最重要方面。但是在处理观测数目小于变量数目时无法发挥作用,例如基因数据。
R语言中进行主成分分析可以采用基本的princomp函数,将结果输入到summary和plot函数中可分别得到分析结果和碎石图。但psych扩展包更具灵活性。
一 、选择主成分个数
选择主成分个数通常有如下几种评判标准:
根据经验与理论进行选择
根据累积方差贡献率 ,例如选择使累积方差贡献率达到80%的主成分个数。
另一种较为先进的方法是平行分析(parallel analysis)。该方法首先生成若干组与原始数据结构相同的随机矩阵,求出其特征值并进行平均,然后和真实数据的特征值进行比对,根据交叉点的位置来选择主成分个数。我们选择USJudgeRatings数据集举例,首先加载psych包,然后使用fa.parallel函数绘制下图,从图中可见第一主成分位于红线上方,第二主成分位于红线下方,因此主成分数目选择1。
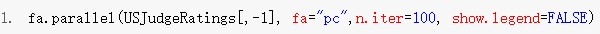
二 、提取主成分

从上面的结果观察到,PC1即观测变量与主成分之间的相关系数,h2是变量能被主成分解释的比例,u2则是不能解释的比例。主成分解释了92%的总方差。注意此结果与princomp函数结果不同,princomp函数返回的是主成分的线性组合系数,而principal函数返回原始变量与主成分之间的相关系数,这样就和因子分析的结果意义相一致。
三 、旋转主成分
旋转是在保持累积方差贡献率不变条件下,将主成分负荷进行变换,以方便解释。成分旋转这后各成分的方差贡献率将重新分配,此时就不可再称之为“主成分”而仅仅是“成分”。旋转又可分为正交旋转和斜交旋转。正交旋转的流行方法是方差最大化,需要在principal中增加rotate='varimax'参数加以实现。也有观点认为主成分分析一般不需要进行旋转。
四、计算主成分得分
主成分得分是各变量的线性组合,在计算出主成分得分之后,还可以将其进行回归等做进一步分析处理。但注意如果输入数据不是原始数据时,则无法计算主成分得分。我们需要在principal中增加score=T的参数设置,结果将存放在结果的score元素中。
R语言多元分析系列之二:探索性因子分析
探索性因子分析(Exploratory Factor Analysis,EFA)是一项用来找出多元观测变量的本质结构、并进行处理降维的技术。 因而EFA能够将具有错综复杂关系的变量综合为少数几个核心因子。EFA和PCA的区别在于:PCA中的主成分是原始变量的线性组合,而EFA中的原始变量是公共因子的线性组合,因子是影响变量的潜在变量,变量中不能被因子所解释的部分称为误差,因子和误差均不能直接观察到。进行EFA需要大量的样本,一般经验认为如何估计因子的数目为N,则需要有5N到10N的样本数目。
虽然EFA和PCA有本质上的区别,但在分析流程上有相似之处。下面我们用ability.cov这个心理测量数据举例,其变量是对人的六种能力,例如阅读和拼写能力进行了测验,其数据是一个协方差矩阵而非原始数据。R语言中stats包中的factanal函数可以完成这项工作,但这里我们使用更为灵活的psych包。
一、选择因子个数
一般选择因子个数可以根据相关系数矩阵的特征值,特征值大于0则可选择做为因子。我们仍使用平行分析法(parallel analysis)。该方法首先生成若干组与原始数据结构相同的随机矩阵,求出其特征值并进行平均,然后和真实数据的特征值进行比对,根据交叉点的位置来选择因子个数。根据下图我们可以观察到特征值与红线的关系,有两个因子都位于红线上方,显然应该选择两个因子。

二、提取因子
psych包中是使用fa函数来提取因子,将nfactors参数设定因子数为2,rotate参数设定了最大化方差的因子旋转方法,最后的fm表示分析方法,由于极大似然方法有时不能收敛,所以此处设为迭代主轴方法。从下面的结果中可以观察到两个因子解释了60%的总方差。Reading和vocabulary这两个变量于第一项因子有关,而picture、blocks和maze变量与第二项因子有关,general变量于两个因子都有关系。

如果采用基本函数factanal进行因子分析,那么函数形式应该是factanal(covmat=correlations,factors=2,rottion='varimax'),这会得到相同的结果。此外,我们还可以用图形来表示因子和变量之间的关系

三、因子得分
得到公共因子后,我们可以象主成分分析那样反过来考察每个样本的因子得分。如果输入的是原始数据,则可以在fa函数中设置score=T参数来获得因子得分。如果象上面例子那样输入的是相关矩阵,则需要根据因子得分系数来回归估计。

参考资料:R in Action
R语言多元分析系列之三:多维标度分析
多维标度分析(MDS)是一种将多维空间的研究对象简化到低维空间进行定位、分析和归类,同时又保留对象间原始关系的数据分析方法。
设想一下如果我们在欧氏空间中已知一些点的座标,由此可以求出欧氏距离。那么反过来,已知距离应该也能得到这些点之间的关系。这种距离可以是古典的欧氏距离,也可以是广义上的“距离”。MDS就是在尽量保持这种高维度“距离”的同时,将数据在低维度上展现出来。从这种意义上来讲,主成分分析也是多维标度分析的一个特例。
一、距离的度量
多元分析中常用有以下几种距离,即绝对值距离、欧氏距离(euclidean)、马氏距离(manhattan)、 两项距离(binary)、明氏距离(minkowski)。在R中通常使用disk函数得到样本之间的距离。MDS就是对距离矩阵进行分析,以展现并解释数据的内在结构。
在经典MDS中,距离是数值数据表示,将其看作是欧氏距离。在R中stats包的cmdscale函数实现了经典MDS。它是根据各点的欧氏距离,在低维空间中寻找各点座标,而尽量保持距离不变。
非度量MDS方法中,“距离"不再看作数值数据,而只是顺序数据。例如在心理学实验中,受试者只能回答非常同意、同意、不同意、非常不同意这几种答案。在这种情况下,经典MDS不再有效。Kruskal在1964年提出了一种算法来解决这个问题。在R中MASS包的isoMDS函数可以实现这种算法,另一种流行的算法是由sammon函数实现的。
二、经典MDS
下面我们以HSAUR2包中的watervoles数据来举例。该数据是一个相似矩阵,表示了不同地区水田鼠的相似程度。首先加载数据然后用cmdscales进行分析。

下面计算前两个特征值在所有特征值中的比例,这是为了检测能否用两个维度的距离来表示高维空间中距离,如果达到了0.8左右则表示是合适的。

然后从结果中提取前两个维度的座标,用ggplot包进行绘图。

三、非度量MDS
第二例子中的数据是关于新泽西州议员投票行为的相似矩阵,这里我们用MASS包中的isoMDS函数进行分析

参考资料:
A Handbook of Statistical Analyses Using R
多元统计分析及R语言建模
R语言多元分析系列之四:判别分析
判别分析(discriminant analysis)是一种分类技术。它通过一个已知类别的“训练样本”来建立判别准则,并通过预测变量来为未知类别的数据进行分类。
判别分析的方法大体上有三类,即Fisher判别、Bayes判别和距离判别。Fisher判别思想是投影降维,使多维问题简化为一维问题来处理。选择一个适当的投影轴,使所有的样品点都投影到这个轴上得到一个投影值。对这个投影轴的方向的要求是:使每一组内的投影值所形成的组内离差尽可能小,而不同组间的投影值所形成的类间离差尽可能大。Bayes判别思想是根据先验概率求出后验概率,并依据后验概率分布作出统计推断。距离判别思想是根据已知分类的数据计算各类别的重心,对未知分类的数据,计算它与各类重心的距离,与某个重心距离最近则归于该类。

一.线性判别
当不同类样本的协方差矩阵相同时,我们可以在R中使用MASS包的lda函数实现线性判别。lda函数以Bayes判别思想为基础。当分类只有两种且总体服从多元正态分布条件下,Bayes判别与Fisher判别、距离判别是等价的。本例使用iris数据集来对花的品种进行分类。首先载入MASS包,建立判别模型,其中的prior参数表示先验概率。然后利用table函数建立混淆矩阵,比对真实类别和预测类别。

二.二次判别
当不同类样本的协方差矩阵不同时,则应该使用二次判别。
model2=qda(Species~.,data=iris,cv=T)
这里将CV参数设置为T,是使用留一交叉检验(leave-one-out cross-validation),并自动生成预测值。这种条件下生成的混淆矩阵较为可靠。此外还可以使用predict(model)$posterior提取后验概率。
在使用lda和qda函数时注意:其假设是总体服从多元正态分布,若不满足的话则谨慎使用。
参考资料:
Modern Applied Statistics With S
Data_Analysis_and_Graphics_Using_R__An_Example_Based_Approach
R语言多元分析系列之五:聚类分析
聚类分析(Cluster Analysis)是根据“物以类聚”的道理,对样品或指标进行分类的一种多元统计分析方法,它是在没有先验知识的情况下,对样本按各自的特性来进行合理的分类。
聚类分析被应用于很多方面,在商业上,聚类分析被用来发现不同的客户群,并且通过购买模式刻画不同的客户群的特征;在生物上,聚类分析被用来动植物分类和对基因进行分类,获取对种群固有结构的认识;在因特网应用上,聚类分析被用来在网上进行文档归类来修复信息。
聚类分析有两种主要计算方法,分别是凝聚层次聚类(Agglomerative hierarchical method)和K均值聚类(K-Means)。
一、层次聚类
层次聚类又称为系统聚类,首先要定义样本之间的距离关系,距离较近的归为一类,较远的则属于不同的类。可用于定义“距离”的统计量包括了欧氏距离(euclidean)、马氏距离(manhattan)、 两项距离(binary)、明氏距离(minkowski)。还包括相关系数和夹角余弦。
层次聚类首先将每个样本单独作为一类,然后将不同类之间距离最近的进行合并,合并后重新计算类间距离。这个过程一直持续到将所有样本归为一类为止。在计算类间距离时则有六种不同的方法,分别是最短距离法、最长距离法、类平均法、重心法、中间距离法、离差平方和法。
下面我们用iris数据集来进行聚类分析,在R语言中所用到的函数为hclust。首先提取iris数据中的4个数值变量,然后计算其欧氏距离矩阵。然后将矩阵绘制热图,从图中可以看到颜色越深表示样本间距离越近,大致上可以区分出三到四个区块,其样本之间比较接近。

然后使用hclust函数建立聚类模型,结果存在model1变量中,其中ward参数是将类间距离计算方法设置为离差平方和法。使用plot(model1)可以绘制出聚类树图。如果我们希望将类别设为3类,可以使用cutree函数提取每个样本所属的类别。

为了显示聚类的效果,我们可以结合多维标度和聚类的结果。先将数据用MDS进行降维,然后以不同的的形状表示原本的分类,用不同的颜色来表示聚类的结果。可以看到setose品种聚类很成功,但有一些virginica品种的花被错误和virginica品种聚类到一起。

二、K均值聚类
K均值聚类又称为动态聚类,它的计算方法较为简单,也不需要输入距离矩阵。首先要指定聚类的分类个数N,随机取N个样本作为初始类的中心,计算各样本与类中心的距离并进行归类,所有样本划分完成后重新计算类中心,重复这个过程直到类中心不再变化。
在R中使用kmeans函数进行K均值聚类,centers参数用来设置分类个数,nstart参数用来设置取随机初始中心的次数,其默认值为1,但取较多的次数可以改善聚类效果。model2$cluster可以用来提取每个样本所属的类别。
model2=kmeans(data,centers=3,nstart=10)
使用K均值聚类时需要注意,只有在类的平均值被定义的情况下才能使用,还要求事先给出分类个数。一种方法是先用层次聚类以决定个数,再用K均值聚类加以改进。或者以轮廓系数来判断分类个数。改善聚类的方法还包括对原始数据进行变换,如对数据进行降维后再实施聚类。
cluster扩展包中也有许多函数可用于聚类分析,如agnes函数可用于凝聚层次聚类,diana可用于划分层次聚类,pam可用于K均值聚类,fanny用于模糊聚类。
原文链接:http://www.cnblogs.com/wentingtu/archive/2012/03/03/2377971.html

数据分析咨询请扫描二维码
若不方便扫码,搜微信号:CDAshujufenxi
在当今这个数据驱动的时代,几乎每一个业务决策都离不开对数据的深入分析。而其中,指标波动归因分析更是至关重要的一环。无论是 ...
2025-02-18当数据开始说谎:那些年我们交过的学费 你有没有经历过这样的场景?熬了三个通宵做的数据分析报告,在会议上被老板一句"这数据靠 ...
2025-02-17数据分析作为一门跨学科领域,融合了统计学、编程、业务理解和可视化技术。无论是初学者还是有一定经验的从业者,系统化的学习路 ...
2025-02-17挖掘用户价值本质是让企业从‘赚今天的钱’升级为‘赚未来的钱’,同时让用户从‘被推销’变为‘被满足’。询问deepseek关于挖 ...
2025-02-17近来deepseek爆火,看看deepseek能否帮我们快速实现数据看板实时更新。 可以看出这对不知道怎么动手的小白来说是相当友好的, ...
2025-02-14一秒精通 Deepseek,不用找教程,不用买资料,更不用报一堆垃圾课程,所有这么去做的,都是舍近求远,因为你忽略了 deepseek 的 ...
2025-02-12自学 Python 的关键在于高效规划 + 实践驱动。以下是一份适合零基础快速入门的自学路径,结合资源推荐和实用技巧: 一、快速入 ...
2025-02-12“我们的利润率上升了,但销售额却没变,这是为什么?” “某个业务的市场份额在下滑,到底是什么原因?” “公司整体业绩 ...
2025-02-08活动介绍 为了助力大家在数据分析领域不断精进技能,我们特别举办本期打卡活动。在这里,你可以充分利用碎片化时间在线学习,让 ...
2025-02-071、闺女,醒醒,媒人把相亲的带来了。 我。。。。。。。 2、前年春节相亲相了40个, 去年春节相亲50个, 祖宗,今年你想相多少个 ...
2025-02-06在数据科学的广阔领域中,统计分析与数据挖掘占据了重要位置。尽管它们常常被视为有关联的领域,但两者在理论基础、目标、方法及 ...
2025-02-05在数据分析的世界里,“对比”是一种简单且有效的方法。这就像两个女孩子穿同一款式的衣服,效果不一样。 很多人都听过“货比三 ...
2025-02-05当我们只有非常少量的已标记数据,同时有大量未标记数据点时,可以使用半监督学习算法来处理。在sklearn中,基于图算法的半监督 ...
2025-02-05考虑一种棘手的情况:训练数据中大部分样本没有标签。此时,我们可以考虑使用半监督学习方法来处理。半监督学习能够利用这些额 ...
2025-02-04一、数学函数 1、取整 =INT(数字) 2、求余数 =MOD(除数,被除数) 3、四舍五入 =ROUND(数字,保留小数位数) 4、取绝对值 =AB ...
2025-02-03作者:CDA持证人 余治国 一般各平台出薪资报告,都会哀嚎遍野。举个例子,去年某招聘平台发布《中国女性职场现状调查报告》, ...
2025-02-02真正的数据分析大神是什么样的呢?有人认为他们能轻松驾驭各种分析工具,能够从海量数据中找到潜在关联,或者一眼识别报告中的数 ...
2025-02-01现今社会,“转行”似乎成无数职场人无法回避的话题。但行业就像座围城:外行人看光鲜,内行人看心酸。数据分析这个行业,近几年 ...
2025-01-31本人基本情况: 学校及专业:厦门大学经济学院应用统计 实习经历:快手数据分析、字节数据分析、百度数据分析 Offer情况:北京 ...
2025-01-3001专家简介 徐杨老师,CDA数据科学研究院教研副总监,主要负责CDA认证项目以及机器学习/人工智能类课程的研发与授课,负责过中 ...
2025-01-29